成都生物所张勇团队开发植物tRNA大语言模型
来源:生物资源利用中心
时间:2026-04-14
中国科学院成都生物研究所张韬、张勇教授团队及其合作者首次将DNA大语言模型引入植物tRNA功能挖掘,开发出专用于植物tRNA识别与功能预测的人工智能系统——植物tRNA大语言模型(tLLMs)。该研究突破传统生物信息学算法依赖保守结构特征的限制,实现对非典型结构tRNA的高精度识别,为基因组编辑工具开发提供了全新的AI驱动范式。相关成果发表于Trends in Biotechnology。
植物基因组编辑技术已成为现代生物学研究和作物改良的核心工具。然而,传统CRISPR-Cas系统依赖U3或U6启动子表达向导RNA(gRNA),在多重编辑应用中面临两大瓶颈:一是载体容量受限,难以实现高阶多重编辑;二是表达效率不一致,导致编辑效果不稳定。内源性tRNA作为Pol III启动子资源,具有启动子功能与RNA加工单元的双重优势,被视为构建紧凑型高效多重编辑系统的理想选择。然而,全球范围内缺乏系统性的功能性tRNA挖掘方法,尤其是难以识别结构变异较大的非典型tRNA,这限制了其在植物基因组编辑中的广泛应用。
研究团队基于前期构建的基座模型训练tLLM,使其系统学习植物tRNA的序列-结构-功能关联规律,突破了传统生物信息学算法对保守结构特征的依赖,成功实现了对非典型结构tRNA的高精度识别(图1)。借助该模型,团队从植物基因组中挖掘出数千个被传统算法遗漏的功能性tRNA,其中包含大量非典型结构成员;实验验证显示,tLLM预测的17个新型tRNA均展现出基因组编辑活性,预测准确率达100%。这些高活性tRNA广泛跨越拟南芥、水稻、玉米、高粱、大豆、小麦等多个物种,其中AtAsp-tRgtc01和OsAsp-tRgtc01的编辑效率显著优于传统使用的AtGly-tRgcc(图2)。
基于上述发现,团队进一步构建了T-tR-sgR-pT紧凑型多重编辑架构(tRNA-sgRNA-多聚T终止子串联系统),巧妙利用tRNA的双重功能(Pol III启动子+RNA加工单元)。该架构在水稻中成功实现10个内源位点的同时高效编辑(效率达65%-100%),并在大豆毛状根中构建了五重基因编辑系统,平均突变率达78%,性能显著优于传统系统。此外,将tLLM挖掘的强启动子tRNA拓展应用于先导编辑(Prime Editing),在OsIPA1位点将编辑效率从5%大幅提升至75%,在OsACC1位点更实现了100%的精准碱基替换效率,有效突破了传统方法难以编辑位点的技术限制(图3,图4)。
tLLM的建立不仅提供了高效的基因组编辑工具元件,更重要的是确立了"AI预测-实验验证-工程应用"的tRNA功能挖掘新范式。该模型揭示的tRNA序列-功能关联规律,为深入理解Pol III启动子进化与表达调控机制提供了全新视角,也为设计兼顾多重编辑效率与载体稳定性的新一代基因组编辑系统奠定了坚实的理论与技术基础。
何瑶博士、马燕勤博士、吴越超博士及唐旭研究员为论文共同第一作者,中国科学院成都生物研究所张韬研究员、张勇教授及马里兰大学Yiping Qi教授为论文共同通讯作者。研究工作得到了国家科技重大专项、国家自然科学基金、中国科学院成都生物研究所自主部署项目等资助。
原文链接:https://doi.org/10.1016/j.tibtech.2026.02.016
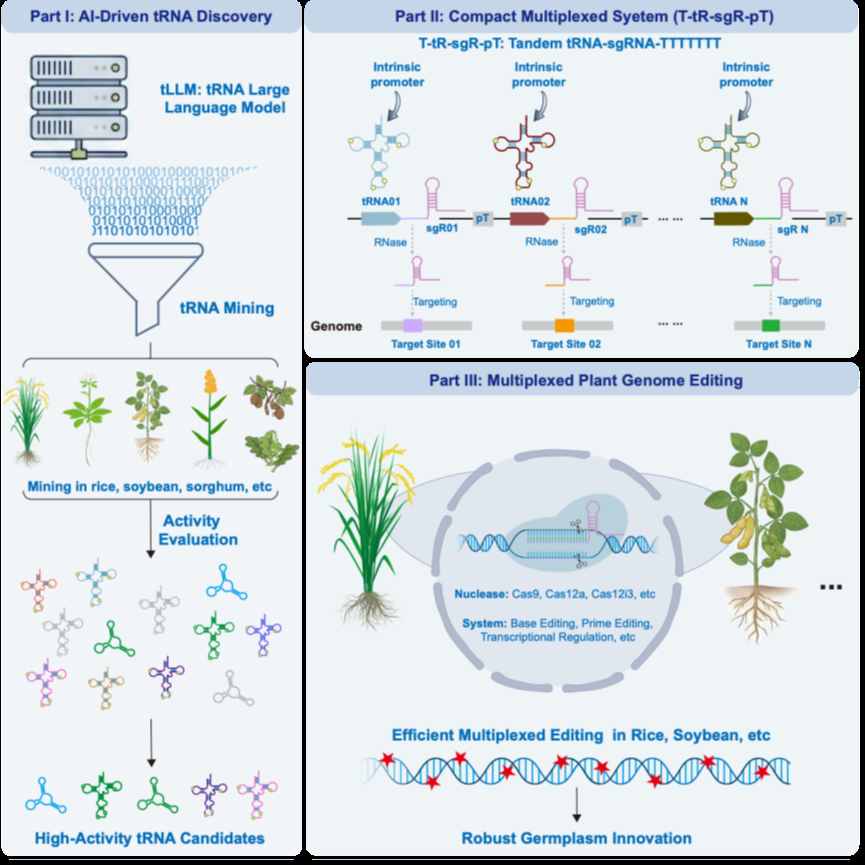
图1 植物tRNA识别与功能预测的人工智能系统实现对非典型结构tRNA的高精度识别为基因组编辑工具开发提供了全新的AI驱动范式
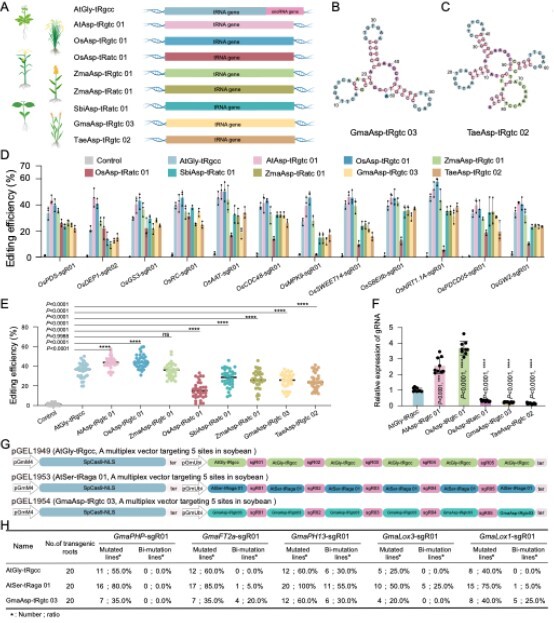
图2 不同植物来源的tRNA在水稻和大豆sgRNA加工和基因组编辑中的比较
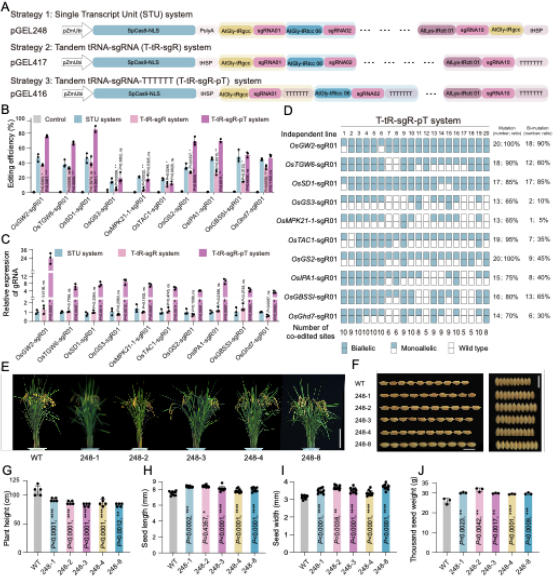
图3水稻Cas9-tRNA多重基因组编辑系统的优化与应用
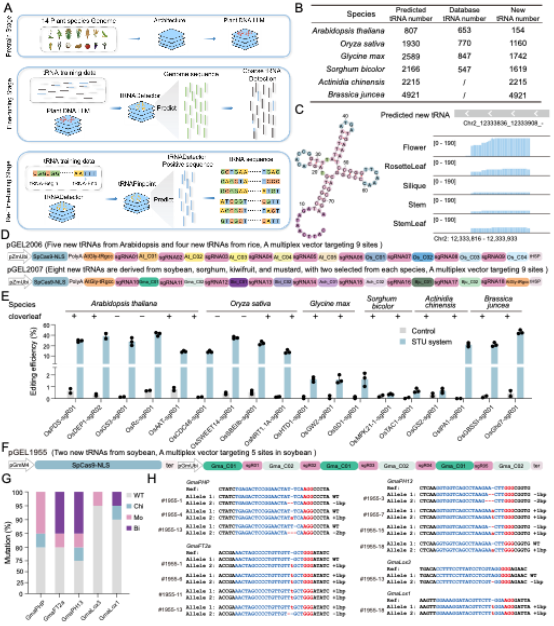
图4用于sgRNA加工和多重基因组编辑的植物tRNA大语言模型的构建和实验验证




